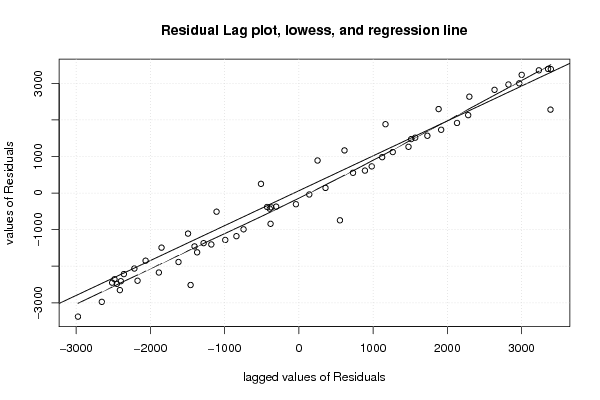
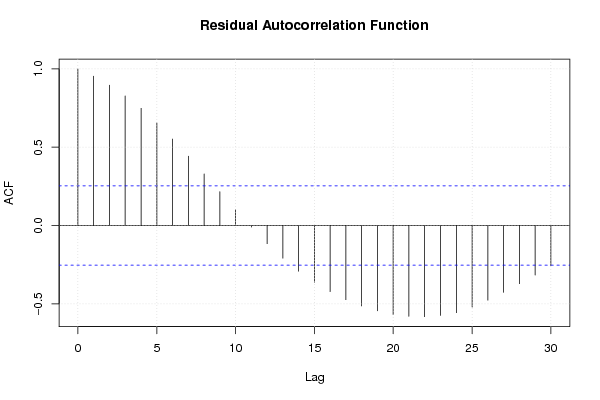
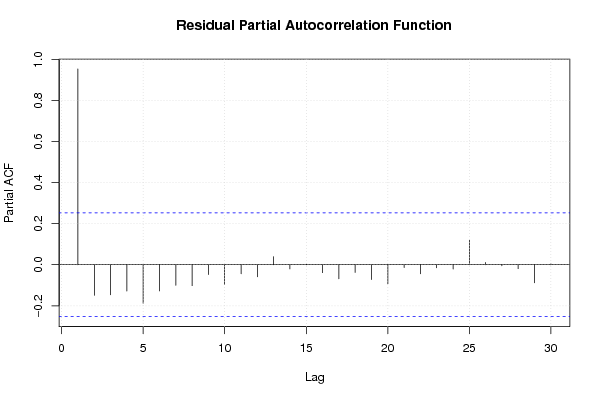
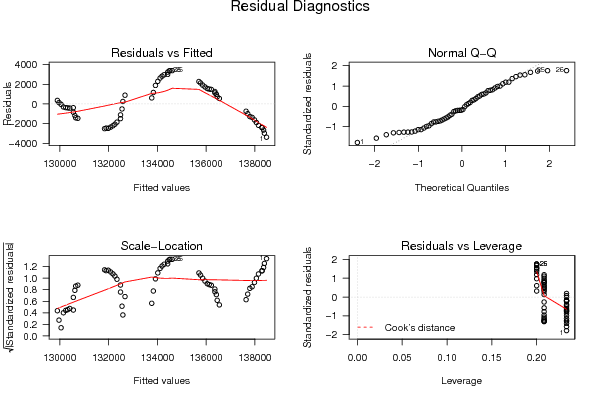
| Multiple Linear Regression - Estimated Regression Equation |
| y[t] = + 139568.525 -934.365972222166M1[t] -861.023611111117M2[t] -734.081250000006M3[t] -634.338888888894M4[t] -474.996527777783M5[t] -458.854166666671M6[t] -383.11180555556M7[t] -301.569444444448M8[t] -235.227083333337M9[t] -169.284722222226M10[t] -94.5423611111136M11[t] -161.142361111112t + e[t] |
| Multiple Linear Regression - Ordinary Least Squares | |||||
| Variable | Parameter | S.D. | T-STAT H0: parameter = 0 | 2-tail p-value | 1-tail p-value |
| (Intercept) | 139568.525 | 1132.34252 | 123.2565 | 0 | 0 |
| M1 | -934.365972222166 | 1377.558048 | -0.6783 | 0.500922 | 0.250461 |
| M2 | -861.023611111117 | 1375.499869 | -0.626 | 0.534362 | 0.267181 |
| M3 | -734.081250000006 | 1373.635049 | -0.5344 | 0.595579 | 0.297789 |
| M4 | -634.338888888894 | 1371.964378 | -0.4624 | 0.645958 | 0.322979 |
| M5 | -474.996527777783 | 1370.488566 | -0.3466 | 0.730447 | 0.365223 |
| M6 | -458.854166666671 | 1369.208241 | -0.3351 | 0.739023 | 0.369511 |
| M7 | -383.11180555556 | 1368.123954 | -0.28 | 0.780686 | 0.390343 |
| M8 | -301.569444444448 | 1367.23617 | -0.2206 | 0.826384 | 0.413192 |
| M9 | -235.227083333337 | 1366.545273 | -0.1721 | 0.864072 | 0.432036 |
| M10 | -169.284722222226 | 1366.051561 | -0.1239 | 0.901905 | 0.450952 |
| M11 | -94.5423611111136 | 1365.755248 | -0.0692 | 0.945105 | 0.472553 |
| t | -161.142361111112 | 16.426294 | -9.81 | 0 | 0 |
| Multiple Linear Regression - Regression Statistics | |
| Multiple R | 0.820999691173647 |
| R-squared | 0.674040492907223 |
| Adjusted R-squared | 0.590816788968642 |
| F-TEST (value) | 8.09914076168326 |
| F-TEST (DF numerator) | 12 |
| F-TEST (DF denominator) | 47 |
| p-value | 6.03553863554041e-08 |
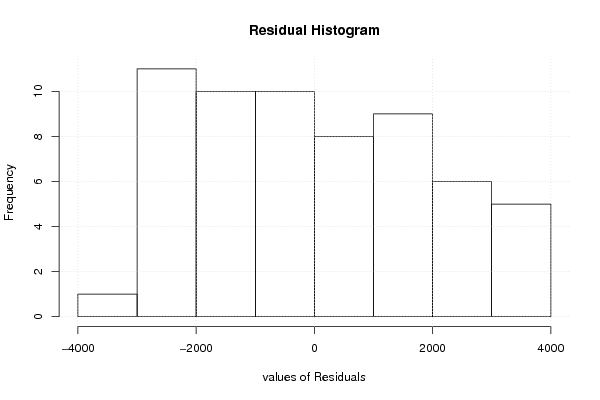
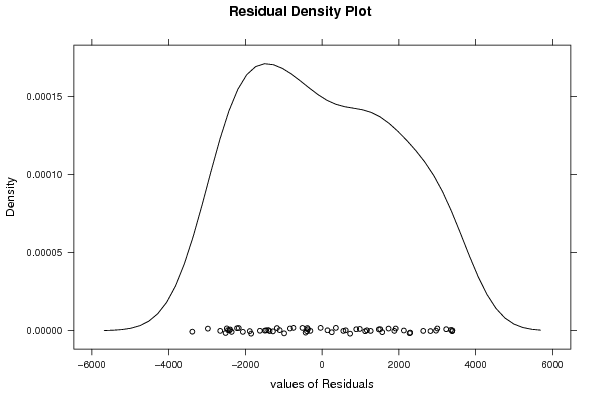
| Multiple Linear Regression - Residual Statistics | |
| Residual Standard Deviation | 2159.29246189414 |
| Sum Squared Residuals | 219139564.991665 |
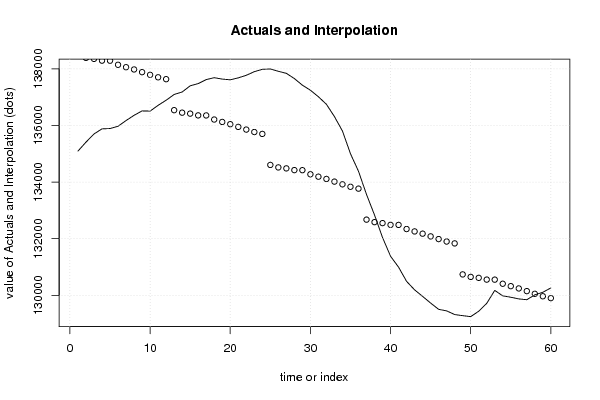
| Multiple Linear Regression - Actuals, Interpolation, and Residuals | |||
| Time or Index | Actuals | Interpolation Forecast | Residuals Prediction Error |
| 1 | 135094 | 138473.016666666 | -3379.01666666643 |
| 2 | 135411 | 138385.216666667 | -2974.21666666668 |
| 3 | 135698 | 138351.016666667 | -2653.01666666668 |
| 4 | 135880 | 138289.616666667 | -2409.61666666668 |
| 5 | 135891 | 138287.816666667 | -2396.81666666668 |
| 6 | 135971 | 138142.816666667 | -2171.81666666668 |
| 7 | 136173 | 138057.416666667 | -1884.41666666668 |
| 8 | 136358 | 137977.816666667 | -1619.81666666668 |
| 9 | 136514 | 137883.016666667 | -1369.01666666668 |
| 10 | 136506 | 137787.816666667 | -1281.81666666668 |
| 11 | 136711 | 137701.416666667 | -990.416666666678 |
| 12 | 136891 | 137634.816666667 | -743.816666666678 |
| 13 | 137094 | 136539.308333333 | 554.691666666599 |
| 14 | 137182 | 136451.508333333 | 730.491666666662 |
| 15 | 137400 | 136417.308333333 | 982.691666666661 |
| 16 | 137479 | 136355.908333333 | 1123.09166666666 |
| 17 | 137620 | 136354.108333333 | 1265.89166666666 |
| 18 | 137687 | 136209.108333333 | 1477.89166666666 |
| 19 | 137638 | 136123.708333333 | 1514.29166666666 |
| 20 | 137612 | 136044.108333333 | 1567.89166666666 |
| 21 | 137681 | 135949.308333333 | 1731.69166666666 |
| 22 | 137772 | 135854.108333333 | 1917.89166666666 |
| 23 | 137899 | 135767.708333333 | 2131.29166666666 |
| 24 | 137983 | 135701.108333333 | 2281.89166666666 |
| 25 | 137996 | 134605.6 | 3390.39999999994 |
| 26 | 137913 | 134517.8 | 3395.2 |
| 27 | 137841 | 134483.6 | 3357.4 |
| 28 | 137656 | 134422.2 | 3233.8 |
| 29 | 137423 | 134420.4 | 3002.6 |
| 30 | 137245 | 134275.4 | 2969.6 |
| 31 | 137014 | 134190 | 2824 |
| 32 | 136747 | 134110.4 | 2636.6 |
| 33 | 136313 | 134015.6 | 2297.4 |
| 34 | 135804 | 133920.4 | 1883.6 |
| 35 | 135002 | 133834 | 1168 |
| 36 | 134383 | 133767.4 | 615.599999999998 |
| 37 | 133563 | 132671.891666667 | 891.108333333276 |
| 38 | 132837 | 132584.091666667 | 252.908333333338 |
| 39 | 132041 | 132549.891666667 | -508.891666666662 |
| 40 | 131381 | 132488.491666667 | -1107.49166666666 |
| 41 | 130995 | 132486.691666667 | -1491.69166666666 |
| 42 | 130493 | 132341.691666667 | -1848.69166666666 |
| 43 | 130193 | 132256.291666667 | -2063.29166666666 |
| 44 | 129962 | 132176.691666667 | -2214.69166666666 |
| 45 | 129726 | 132081.891666667 | -2355.89166666666 |
| 46 | 129505 | 131986.691666667 | -2481.69166666666 |
| 47 | 129450 | 131900.291666667 | -2450.29166666666 |
| 48 | 129320 | 131833.691666667 | -2513.69166666666 |
| 49 | 129281 | 130738.183333333 | -1457.18333333339 |
| 50 | 129246 | 130650.383333333 | -1404.38333333332 |
| 51 | 129438 | 130616.183333333 | -1178.18333333332 |
| 52 | 129715 | 130554.783333333 | -839.783333333322 |
| 53 | 130173 | 130552.983333333 | -379.983333333322 |
| 54 | 129981 | 130407.983333333 | -426.983333333323 |
| 55 | 129932 | 130322.583333333 | -390.583333333323 |
| 56 | 129873 | 130242.983333333 | -369.983333333322 |
| 57 | 129844 | 130148.183333333 | -304.183333333323 |
| 58 | 130015 | 130052.983333333 | -37.9833333333228 |
| 59 | 130108 | 129966.583333333 | 141.416666666678 |
| 60 | 130260 | 129899.983333333 | 360.016666666677 |
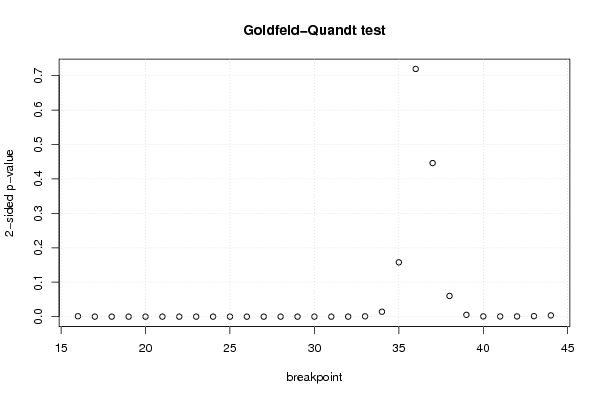
| Goldfeld-Quandt test for Heteroskedasticity | |||
| p-values | Alternative Hypothesis | ||
| breakpoint index | greater | 2-sided | less |
| 16 | 0.00060746734076419 | 0.00121493468152838 | 0.999392532659236 |
| 17 | 3.9371240151208e-05 | 7.87424803024159e-05 | 0.999960628759849 |
| 18 | 2.34577214062529e-06 | 4.69154428125058e-06 | 0.999997654227859 |
| 19 | 7.0797034117476e-07 | 1.41594068234952e-06 | 0.999999292029659 |
| 20 | 6.53332033791137e-07 | 1.30666406758227e-06 | 0.999999346667966 |
| 21 | 3.81620417175415e-07 | 7.63240834350831e-07 | 0.999999618379583 |
| 22 | 8.21849428986936e-08 | 1.64369885797387e-07 | 0.999999917815057 |
| 23 | 2.06219191783918e-08 | 4.12438383567836e-08 | 0.999999979378081 |
| 24 | 6.47694987615527e-09 | 1.29538997523105e-08 | 0.99999999352305 |
| 25 | 1.59266509227882e-09 | 3.18533018455764e-09 | 0.999999998407335 |
| 26 | 1.23092773391168e-09 | 2.46185546782337e-09 | 0.999999998769072 |
| 27 | 3.16312249726122e-09 | 6.32624499452243e-09 | 0.999999996836877 |
| 28 | 1.48080822606901e-08 | 2.96161645213802e-08 | 0.999999985191918 |
| 29 | 8.06953007466768e-08 | 1.61390601493354e-07 | 0.999999919304699 |
| 30 | 4.49742878195913e-07 | 8.99485756391826e-07 | 0.999999550257122 |
| 31 | 3.16925719007608e-06 | 6.33851438015216e-06 | 0.99999683074281 |
| 32 | 3.01133612531012e-05 | 6.02267225062024e-05 | 0.999969886638747 |
| 33 | 0.000474529420544604 | 0.000949058841089208 | 0.999525470579455 |
| 34 | 0.00712147706677037 | 0.0142429541335407 | 0.99287852293323 |
| 35 | 0.0788775173297898 | 0.15775503465958 | 0.92112248267021 |
| 36 | 0.359604308250028 | 0.719208616500055 | 0.640395691749972 |
| 37 | 0.777067293640558 | 0.445865412718884 | 0.222932706359442 |
| 38 | 0.969935719400567 | 0.060128561198865 | 0.0300642805994325 |
| 39 | 0.997388201813103 | 0.00522359637379508 | 0.00261179818689754 |
| 40 | 0.999616613244127 | 0.000766773511746254 | 0.000383386755873127 |
| 41 | 0.999717166014648 | 0.000565667970703645 | 0.000282833985351823 |
| 42 | 0.999640224650686 | 0.000719550698628482 | 0.000359775349314241 |
| 43 | 0.999261670675202 | 0.00147665864959689 | 0.000738329324798444 |
| 44 | 0.99818323887733 | 0.00363352224534003 | 0.00181676112267001 |
| Meta Analysis of Goldfeld-Quandt test for Heteroskedasticity | |||
| Description | # significant tests | % significant tests | OK/NOK |
| 1% type I error level | 24 | 0.827586206896552 | NOK |
| 5% type I error level | 25 | 0.862068965517241 | NOK |
| 10% type I error level | 26 | 0.896551724137931 | NOK |